「最近の研究開発」のページは現在準備中です
最近の研究開発(2021年度までの内容)
2012年以降の研究開発:開発手法は定式化で,理論研究は一文で要約
複数手法に共通する記号
X: n個体×p変数の列中心化されたデータ行列
S: p変数×p変数の標本共分散行列
F: n個体×m因子の得点行列, F’F = nI (単位行列)
A: p変数×m因子の負荷行列, m ≤ min(n, p)
U: n個体×p変数の得点行列, U’U = nI, F’U= O (零行列)
Ψ: p変数×p変数の対角行列
因子分析
- 行列因子分析の解法: min F, A, U, Ψ ||X–FA’-UΨ||2のA, Ψの解を,Sだけから求めるアルゴリズム (Adachi, 2012).
- EMアルゴリズム: 不適解を与えないことを証明 (Adachi, 2013).
- スパース因子分析: min F, A, U, Ψ||X–FA’-UΨ||2 s.t. Aの零要素数=定数. ペナルティを使わないのが特徴 (Adachi & Trendaifilov 2015).
- 一般化最小二乗法: Majorizationを使ったmin A, Ψ tr{(S–AA’-Ψ2)Ψ–2}2 (Adachi, 2015).
- カテゴリカル因子分析: min F, A, U, Ψ, Q Σj||GjQj–FAj‘–UjΨj||2 s.t. Qj‘Gj‘GjQj=nI, GkQkは列中心化.ここで,Gkはn個体×Kjカテゴリーのメンバーシップデータ行列 (Makino, 2015).
- クラスタリング因子分析: min F, A, Ψ nlog|Ψ2|+ tr(X–GCA’)Ψ–2(X–GCA’)’ s.t. F=GC. ここで,G はn個体×g群の未知メンバーシップ行列 (Uno, Satomura, & Adachi, 2016).
主成分分析
- 一般化同時プロクラステス分析: min N, F, A Σk(n–1||FkNk–F||2+p–1||AkNk–1–A||2).
ここで,Xk≅FkAk‘=FkNkNk–1Ak‘ (Adachi, 2015). - スパース主成分分析: min F, A ||X–FA’||2 over F, A s.t. Aの零要素数=定数 (Adachi & Trendaifilov 2016).
- スパースTucker2: min F, A ||Z–FH(I⊗M’)||2 s.t. Hの零要素数=定数. ここで,Zは三相データのスライスを横に並べた行列 (Ikemoto & Adachi, 2016).
正準相関分析
- 再定式化: maxA,B tr{XA(A’X’XA)–1A’X’}{YB(B’Y’YB)–1B’Y’} s.t. rank(XA)=rank(YB)≤min(p, q)と定式化できること(斜交回転可能)を証明. ここで, [X, Y]はn ×(p+q)のデータ行列 (Satomura & Adachi, 2013).
文献はこちらをクリック
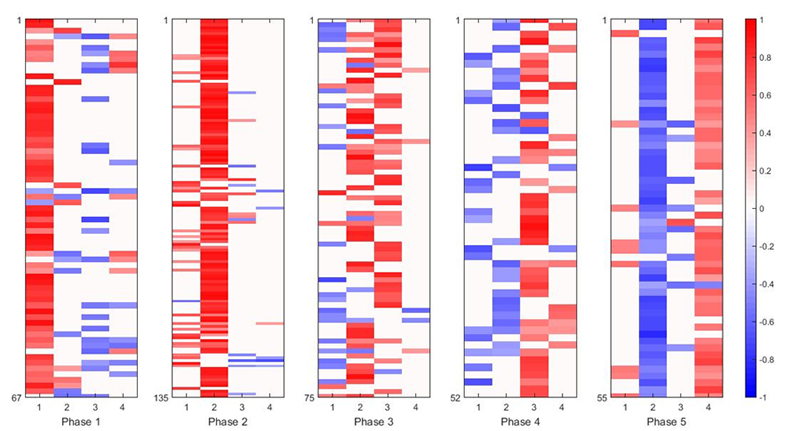
遺伝子表現データに対する[8]のAの解
